 您的购物车当前为空
您的购物车当前为空
库设计
分子对接
对接模型基于已报道的PDB蛋白结构3O8Y、4NRE和3D3L构建。在对接前,所有结构均经过优化和重建,以修正结构间隙和缺失的侧链(图1)。与Fe3+离子配位的水分子位置受到限制,其电离状态被设定。每个对接模型均包含结合位点的静电描述符以及必需的位置约束。
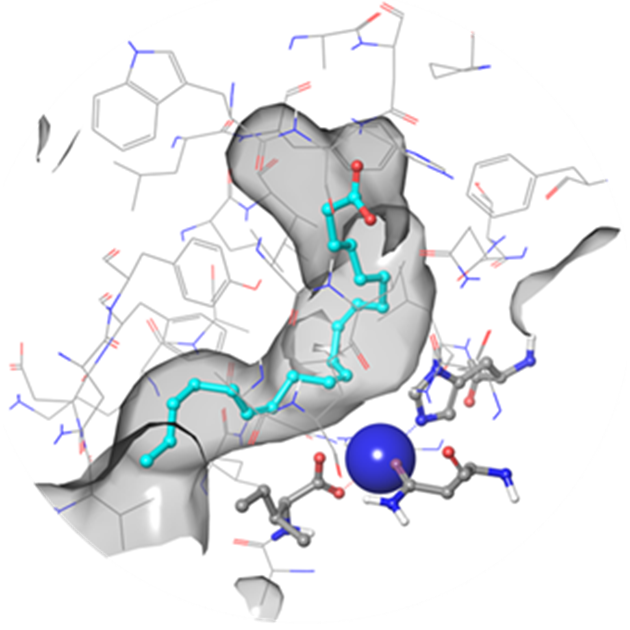
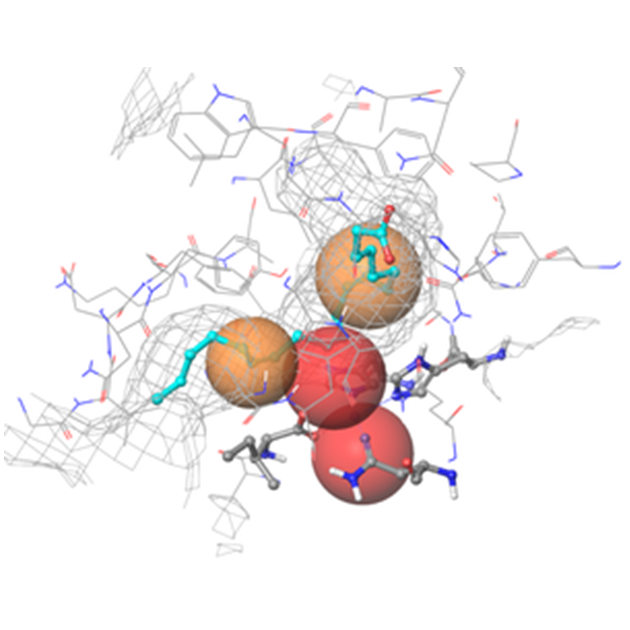
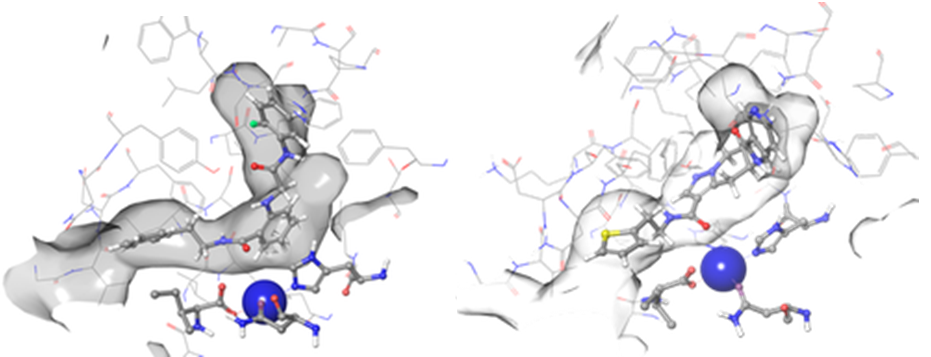
所得模型被用于筛选Enamine公司全库存(超过470万种化合物)中约100万分子的MedChem精炼子集。命中化合物被定义为必须满足位置约束条件——金属配位(红色标注)和疏水中心(橙色标注)(图2)。通过比较对接评分及结合构象的目视检查(氢键存在情况、水暴露程度)来评估对接结果,最终筛选出950种化合物(图3)。
相似性搜索
• 在ChEMBL数据库中对脂氧合酶靶点进行搜索,得到包含322个活性化合物的参考集,涵盖三种脂氧合酶类型(A5、A12、A15)。通过效力值阈值(IC50 ≤ 1μM)和药物化学毒性基团过滤器进一步筛选了这些化合物。
• 使用线性指纹和Tanimoto算法,以0.85的阈值进行了二维相似性搜索。
• 从Enamine的筛选库中筛选出近500种化合物,并添加到LOX文库中。





 很棒
很棒

 |
|