 您的购物车当前为空
您的购物车当前为空
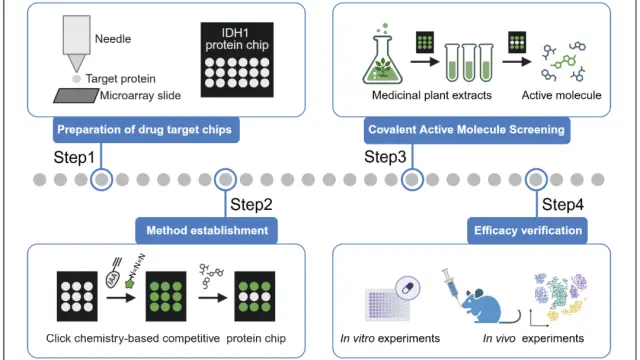
虚拟筛选的方法介绍
虚拟筛选是基于药物设计理论,利用计算机技术和专业应用软件,从大量化合物中筛选出具有潜在活性的候选化合物后,对其进行实验验证的一种方法,是现代药物发现中常用的先导化合物筛选技术之一。
虚拟筛选与高通量筛选特点对比
与传统的高通量筛选相比,虚拟筛选具有明显的优势。它能够综合考虑包括化合物的理化性质、ADMET 参数等多种因素,提供更全面的评估。虚拟筛选无需制备和测试海量的实体化合物,从而大幅提升实验的速度和效率。此外,虚拟筛选成功获得活性化合物的概率明显高于高通量筛选。

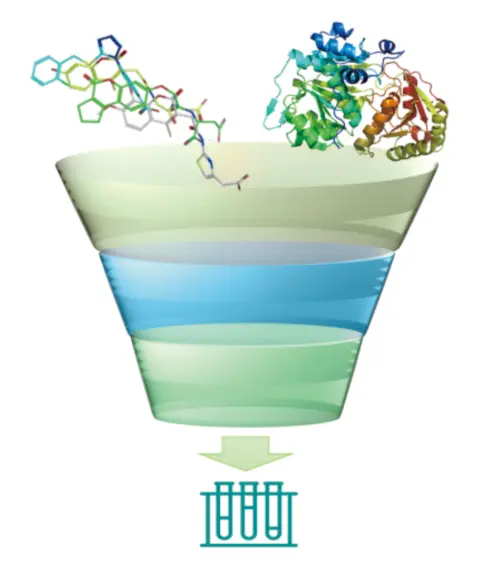
虚拟筛选的方法
虚拟筛选根据药物设计原理主要分为两种方法:基于配体的筛选方法 和 基于受体的筛选方法。
1)基于配体的筛选
利用已知活性分子的化学信息,通过相似性搜索筛选潜在活性分子。
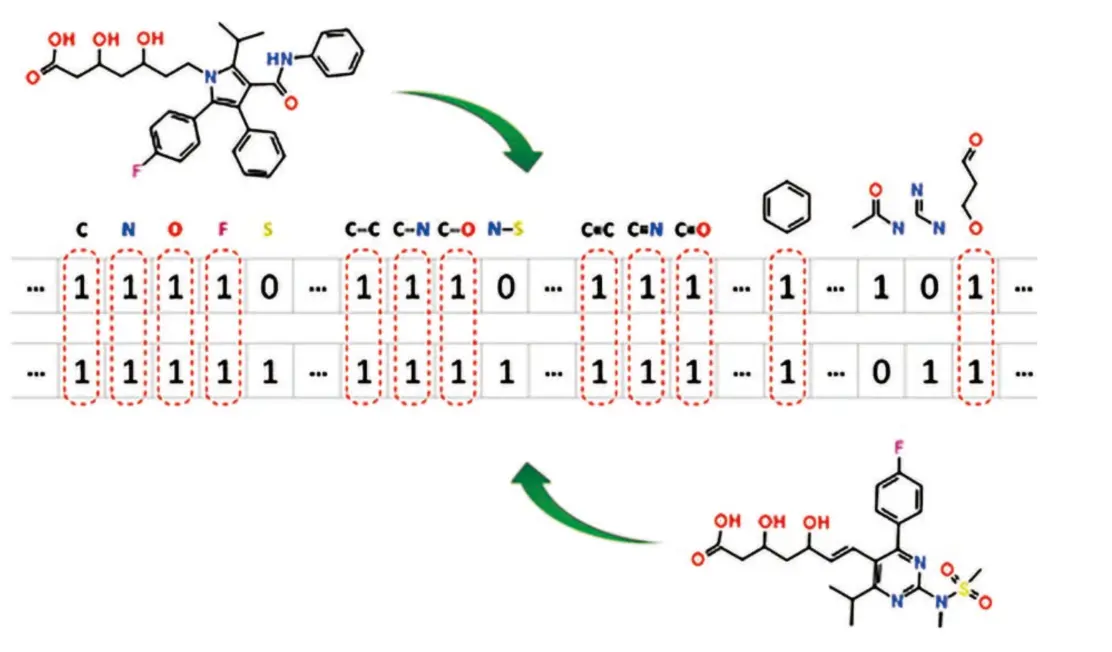
• 基于2D 结构相似性的筛选方法
利用已知活性分子作为模板,通过化学结构相似性搜索的方法筛选潜在活性分子。
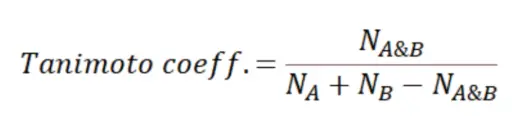
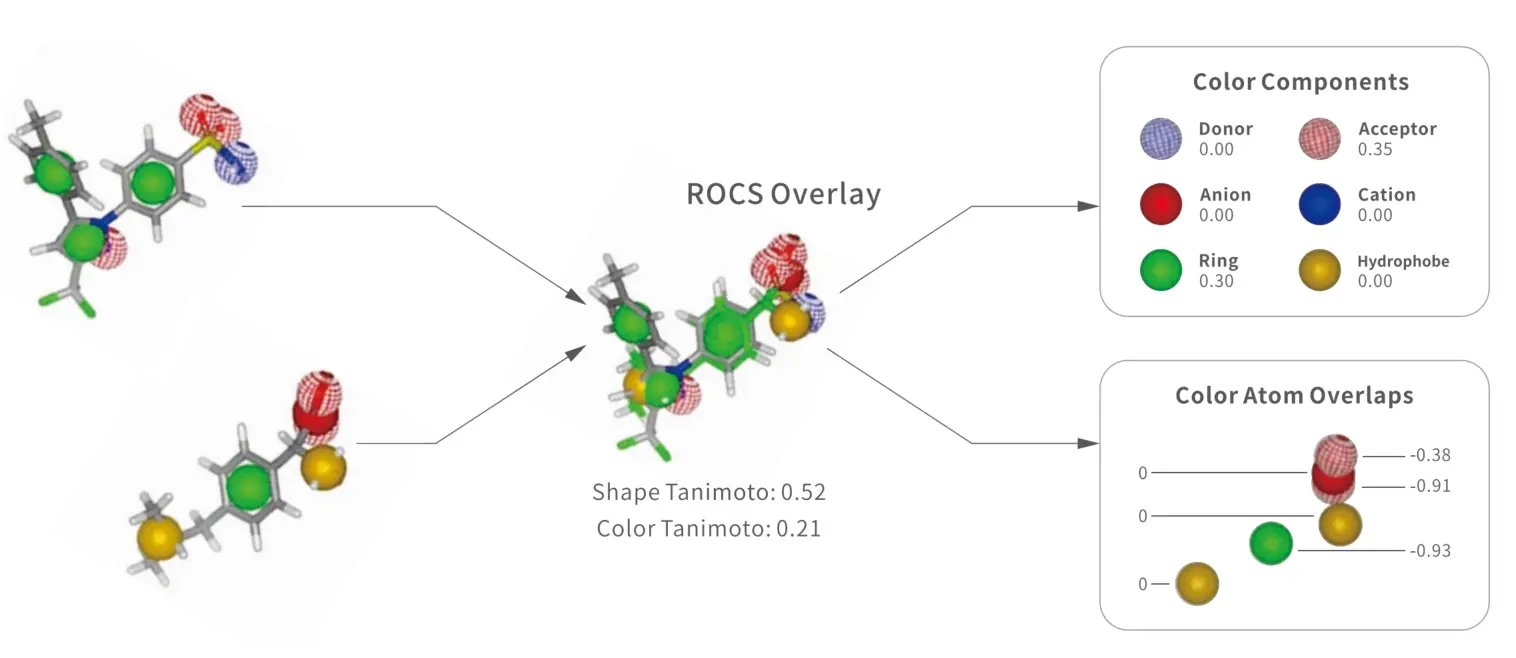
• 基于3D 结构相似性的筛选方法
利用分子的三维形状,药效团特征计算待筛小分子化合物与参照化合物的相似度
2)基于受体的筛选
基于受体的三维结构,在结合位点处自动匹配小分子,然后对可能的结合模式进行结合能计算,从中挑选候选化合物。在此基础上衍生出多种虚拟筛选策略:
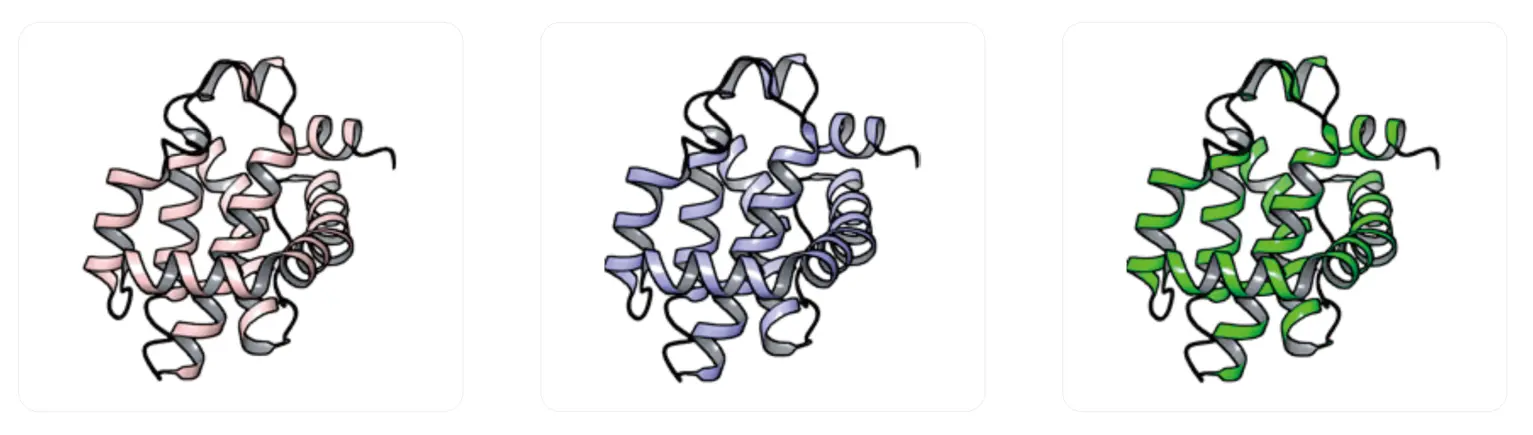
• 基于多构象的虚拟筛选
考虑到蛋白柔性的影响,采用多个晶体结构或基于分子动力学模拟所得的若干个典型构象进行平行虚拟筛选可以有效地提高虚拟筛选的成功率。
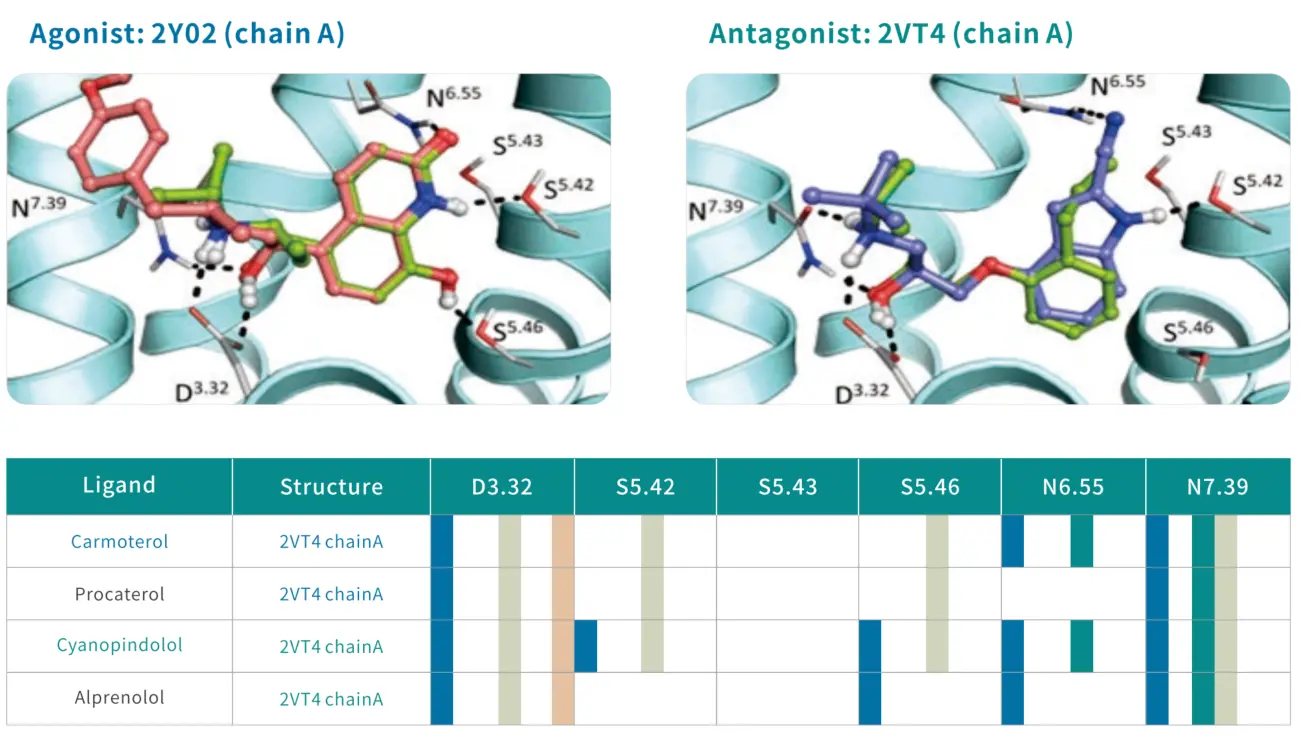
• 基于蛋白-配体分子作用指纹的虚拟筛选
蛋白-配体分子相互作用指纹(Protein-Ligandinteraction fingerprint,PLIF 或IFP)是一种数值化方法,用于记录和描述蛋白质与配体之间不同类型的相互作用。该方法利用二进制编码的思路,将复杂的分子间相互作用转化为简单的一维指纹形式。利用蛋白-配体分子作用指纹策略可以有效区分 GPCR激动剂和拮抗剂。
虚拟筛选合作成功案例
Hyperactivation of HER2-SHCBP1-PLK1 axis promotes tumor cell mitosis and impairs trastuzumabsensitivityto gastric cancer.Nat Commun.2021 May 14;12(1):2812.
IF= 16.6
利用曲妥珠单抗治疗胃癌的过程中,HER2-SHCBP1-PLK1 轴的激活被认为是一个关键的促进肿瘤发生和耐药的因素。为了深入理解并克服这一挑战,研究团队通过结构域截短实验和免疫共沉淀,发现 SHCBP1 的 355-562 氨基酸区域是与 PLK1结合所必需的,并发现与 SHCBP1结合的是 PLK1的 polo-box结构域(PBD)而不是激酶结构域。
为了探索潜在的治疗策略,研究团队在TargetMol的协助下,利用同源模建和分子对接技术,得到了 SHCBP1 和PLK1的结合模式。并通过设计 PLK1的蛋白质缺失突变和氨基酸突变实验进一步验证了这一结合模式。基于这些结构信息,研究人员在TargetMol的协助下进行了虚拟筛选,成功发现 TFBG 作为一种潜在的抑制剂,通过抑制 SHCBP1和 PLK1 的相互作用,展示了抗癌的功能。实验数据表明,TFBG 的 Kd 值低至 0.467 uM,对 SNU-216 胃癌细胞的增殖有明显的抑制作用(IC50=23.42 umol/ml)。
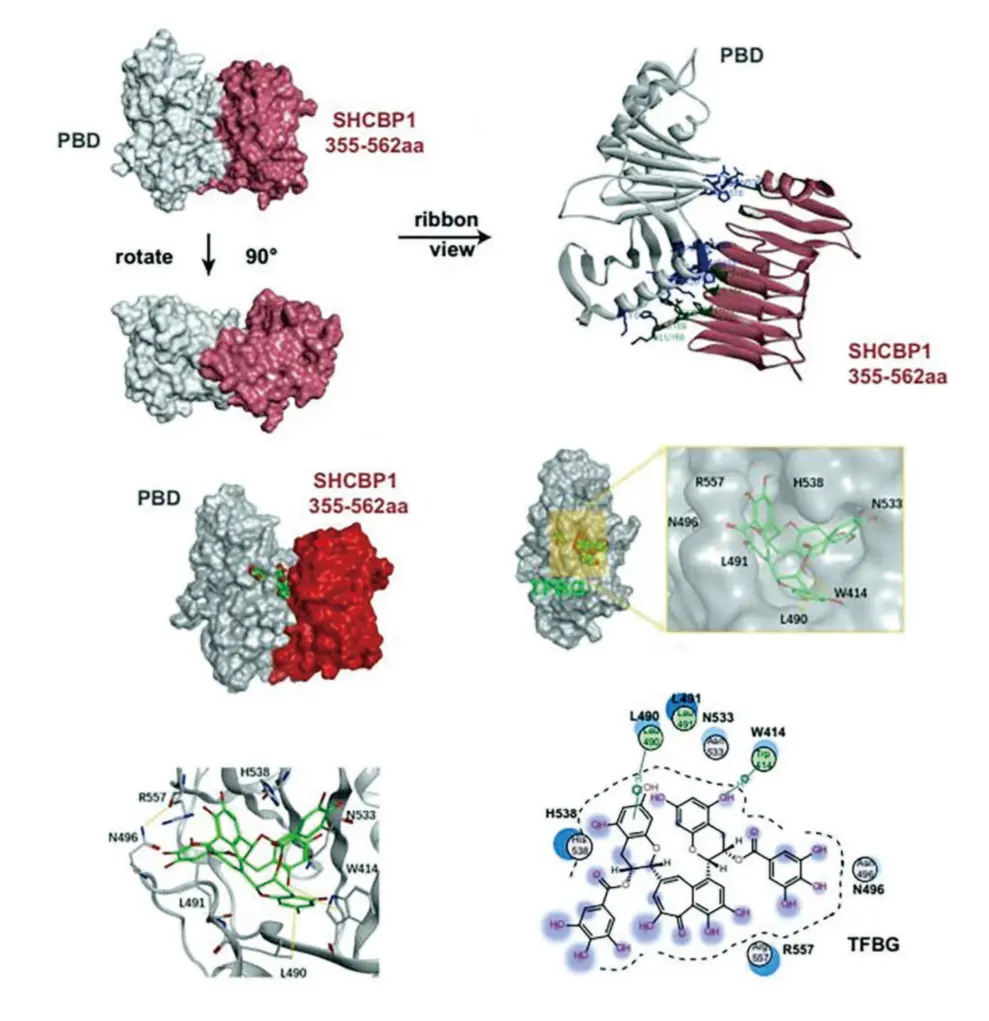
命中分子TFBG与SHCBP1-PLK1复合物的结合模式及相互作用
其他文章
订阅TargetMol新闻
科学新闻、观点和分析的重要汇总,每个工作日都会发送到您的收件箱.




 |
|