库设计
为设计分子库并筛选最具潜力的分子,我们关注结核分枝杆菌(Mtb)细胞壁的复杂性及膜穿透的难点。尽管缺乏某些无明确规则的固定筛选标准,我们仍基于已报道的数据及细胞活性与非活性化合物的结构分析,尽可能排除所有可能存在穿透问题的化合物。
通过研究Mtb固有的生化通路与形态特性相关特征,我们筛选并优先确定了一组蛋白质靶标,用于进行计算机虚拟高通量筛选(vHTS)并选择具有推定活性的化合物。总体上,该库中的蛋白质靶标可分为两大类:
- 细胞壁合成相关蛋白;
- 与真核生物不同的Mtb特异性必需蛋白靶标。
以下为部分关键靶标简介:
• 丙氨酸消旋酶(Alr):催化L-丙氨酸与D-丙氨酸的相互转化,进而参与肽聚糖交联的关键步骤。
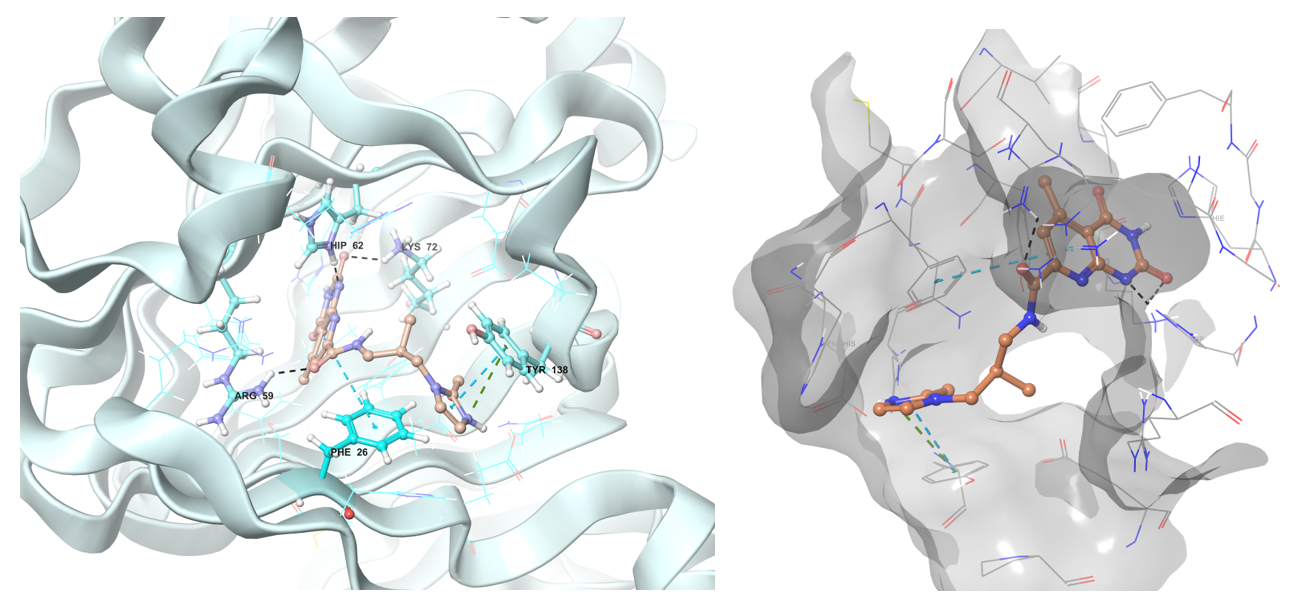
• dTDP-4-脱氢鼠李糖3,5-差向异构酶(RmlC):参与dTDP-L-鼠李糖的生物合成,后者是阿拉伯半乳聚糖的半乳糖区与肽聚糖分子连接所必需的。
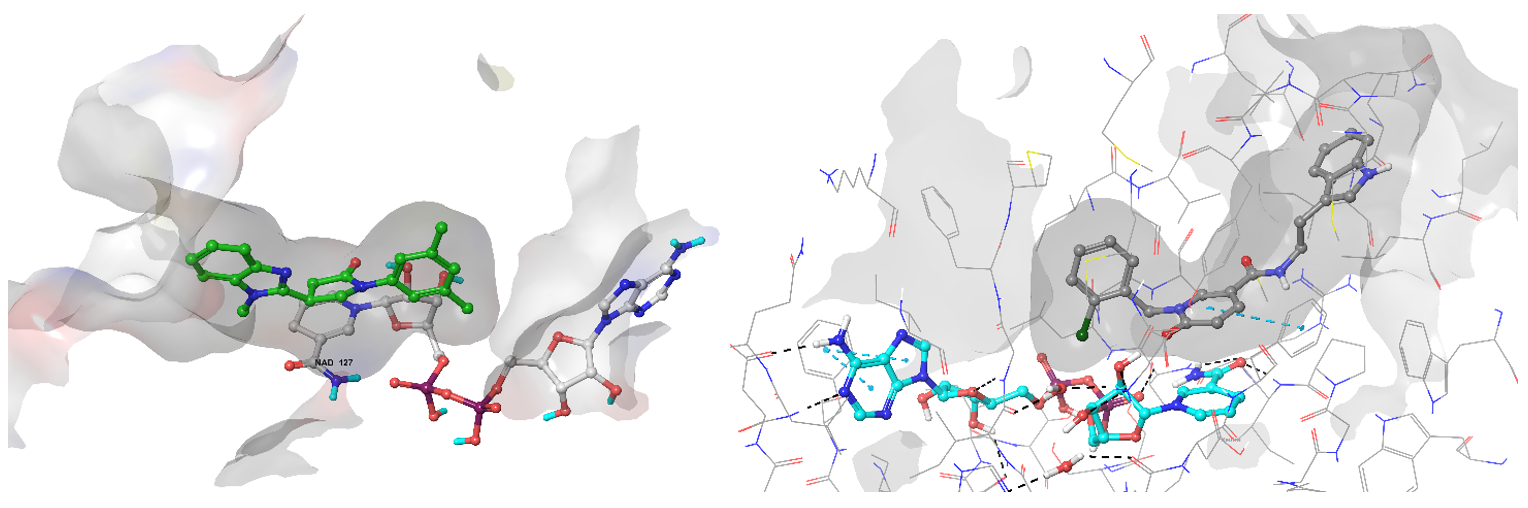
• 烯酰-[酰基载体蛋白]还原酶[NADH](InhA):参与分枝菌酸的生物合成,在脂肪酸延伸过程中起关键作用。
• 十异戊二烯磷酸-β-D-核糖氧化酶(Dpre1):催化十异戊二烯磷酸阿拉伯糖(DPA)形成的复合物组分,DPA是细胞壁阿拉伯聚糖合成的关键前体。
• N-乙酰葡萄糖胺-1-磷酸尿苷转移酶(GLMU):催化UDP-GlcNAc生物合成的最后两步,对脂多糖(LPS)的脂质A合成至关重要。
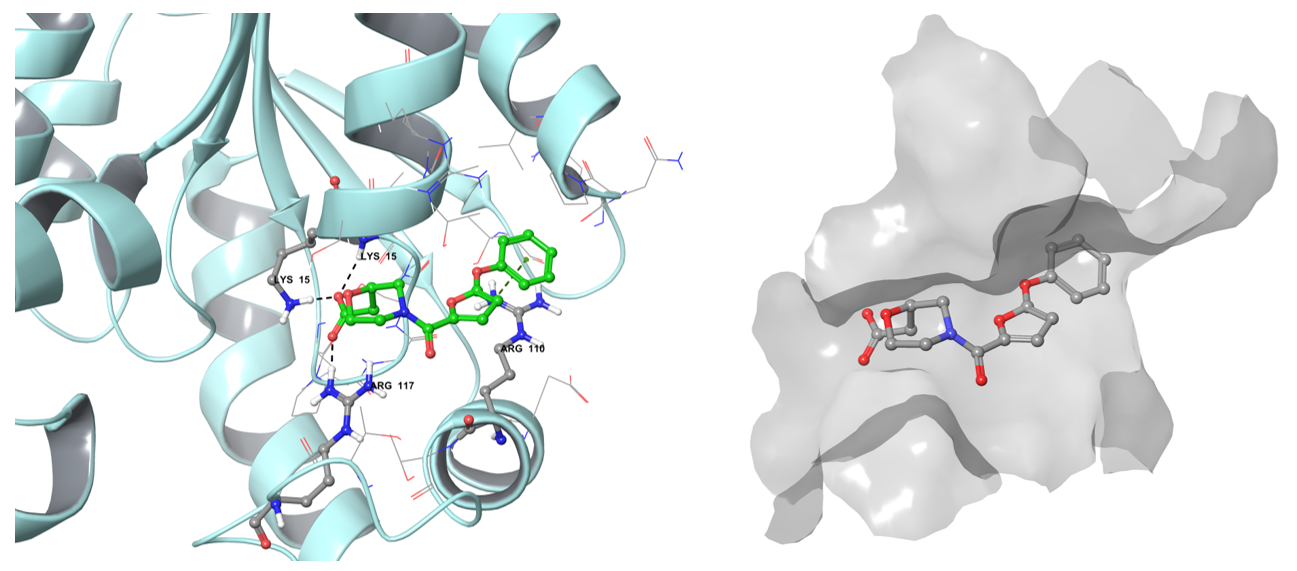
• 莽草酸激酶(AroK):利用ATP磷酸化莽草酸的3-羟基,为芳香族氨基酸和次级代谢物的共同前体合成所必需。氨基酸生物合成因其广泛的酶家族表征,也是药物设计中极具吸引力的方向。
• β-内酰胺酶:负责介导对β-内酰胺类抗生素的耐药性。
• 异柠檬酸裂解酶:负责乙醛酸循环的第一步,即将C2化合物合成为C4二羧酸。
• ATP酶(ClpC、ClpX):作为伴侣蛋白,通过细菌蛋白酶体诱导蛋白质降解,在细菌蛋白质稳态中发挥重要作用。
• Mtb调节性丝氨酸蛋白酶(ClpP1P2):形成细菌蛋白酶体的丝氨酸蛋白酶,负责细菌内蛋白质稳态与降解。
• 肽基tRNA水解酶(Pth):一种必需的Mtb特异性RNA水解酶,参与细菌稳态和蛋白质合成调控。
vHTS流程采用基于网格的结合位点表示方法,并根据文献数据(突变实验)或配体-蛋白质相互作用图谱设定约束条件,进行部分或完全匹配。除依据经验性对接评分对化合物排序外,还对结果构象进行了视觉检查,以评估结合模式的可靠性。同时,针对所选靶标的参考化合物数量相对较少,且每个靶标对应的参考集内部多样性较低。
Z1603549506在莽草酸激酶结合位点的结合姿态示例。
Z1313265676 结合 RmlC 还原酶的预测构象,采用带状和表面形状蛋白质表示。
预测命中物Z111780734(左)和Z189105794在InhA酶活性位点的结合构象示例。
 您的购物车当前为空
您的购物车当前为空