库设计
免疫肿瘤学文库设计中,特别关注了检查点蛋白,例如 PD-1、CTLA-4、CD152、CD279/74 和 PD-L1。
靶点的计算机筛选:
应用了基于结构的方法来寻找 TLR7 和 TLR8 受体的潜在抑制剂。我们分析并叠加了 PDB 中报告的所有相关蛋白质结构,以生成基于蛋白质结构的药效团模型。随后,通过一组已知有效和非活性化合物(参考集)验证了这两个模型。
TLR7 和 TLR8 与共结晶配体的复合物结构(上方一对)。图中展示了通过对接计算发现的先导化合物 Z242112334 在 TLR7 中的结合模式(左),以及另一先导化合物 Z1438692506 在 TLR8 结合空腔中的结合模式(右)。
基于4U97和2WOT结构,分别研究了两种具有已报道激酶活性的跨膜蛋白(IRAK4和TGFβR1)。配体结构需具备多个疏水核,并能与结合位点中的关键氨基酸形成强氢键,这是筛选潜在抑制剂的基本条件。然而,为了涵盖所有可能的结构与构象,在构建这些小型化合物库时,采用了疏水核与氢键的交替组合进行筛选。针对每种激酶,生成了两组约束条件子集,以建立最详尽的筛选模型。
左侧为结晶状态以及与对接分子 Z243559212 结合的 IRAK4;右侧为来自 RCSB 数据库的原始状态以及与 Z316882020 结合的 TGF beta R1。
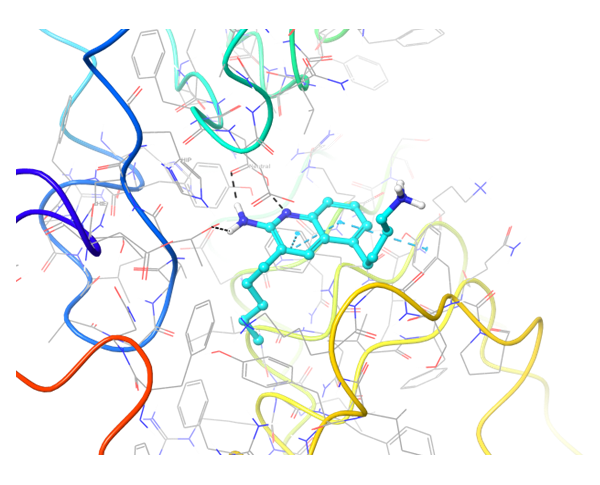
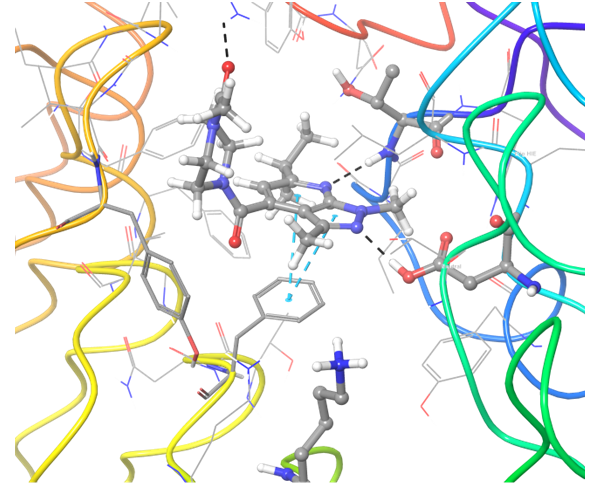
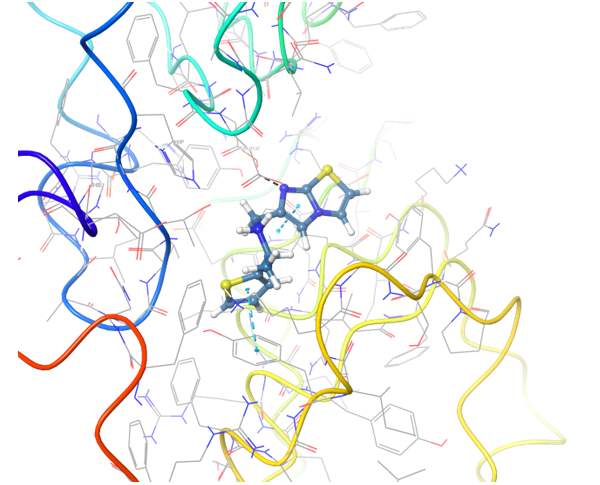
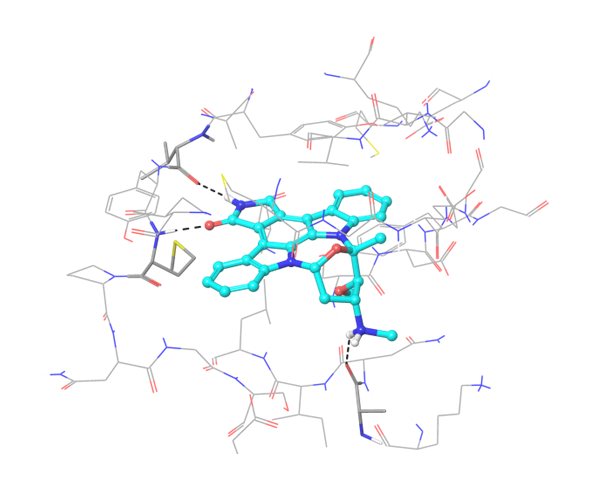
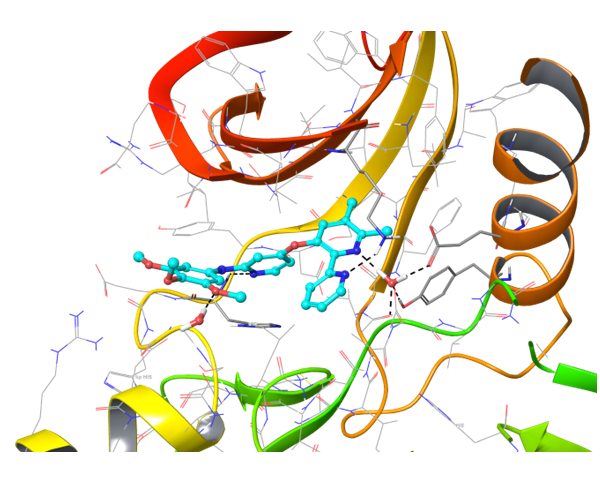
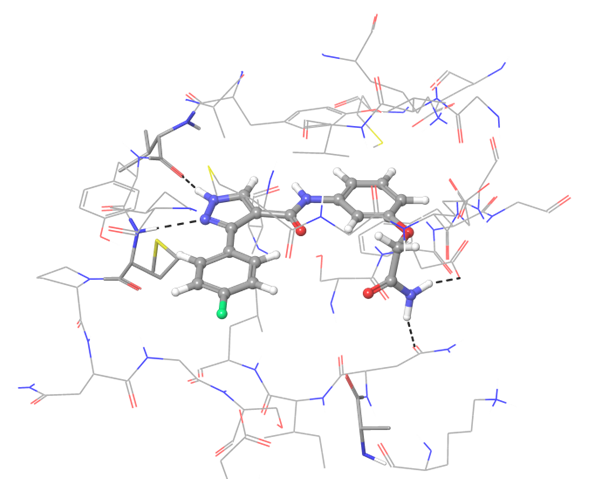
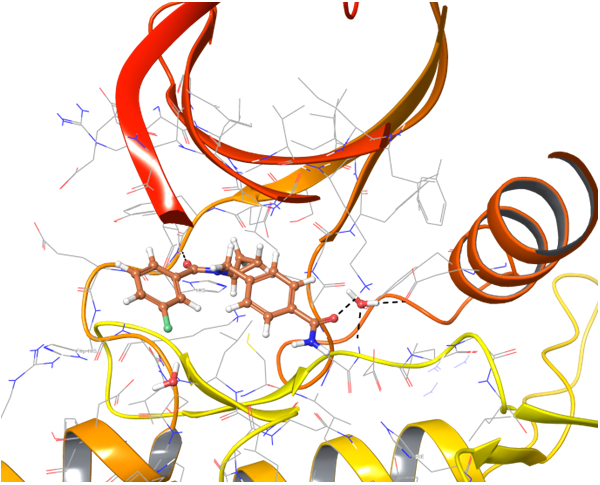
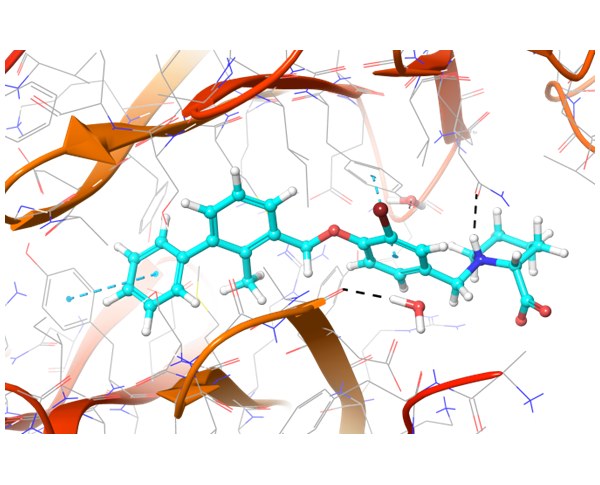
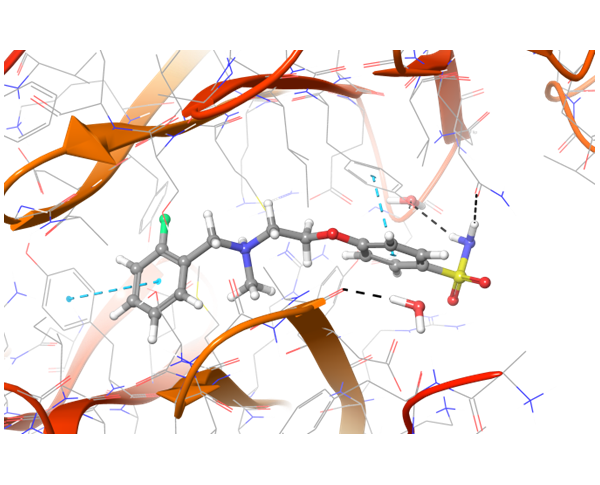
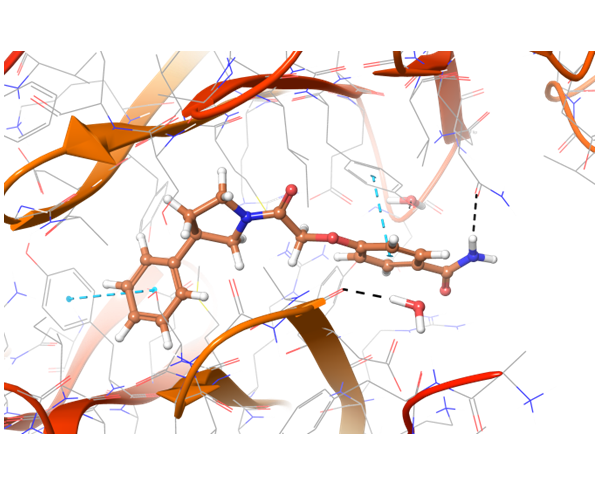
关于PD-1与PD-L1的结合,目前已知的PD-L1抑制剂较少。我们应用了结构与空间限制来寻找能够类似地调节PD-L1结构的化合物。为了提高选择性并同时避免构象相似性,我们进行了两阶段筛选,最终选出了最有效的结合物。
共晶BMS-8结构(左上)及其显示相互作用的图示,以及结构相似、结合模式相近的Z195611316和Z942299126配体。
 您的购物车当前为空
您的购物车当前为空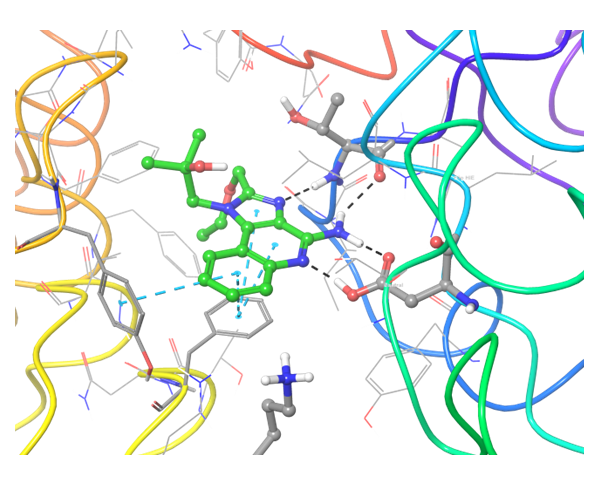



 很棒
很棒


 |
|