 您的购物车当前为空
您的购物车当前为空
库设计
分析了所有可用的SH2结构域结合位点结构,并基于其空间分子形状进行聚类。经过比对分析和聚类,筛选出构象差异最大的结构用于虚拟筛选。分子对接计算使用了Enamine MedChem经过筛选的现货化合物子集(约100万种化合物),并额外挑选了含有拟肽基序的化合物。
对包含在110种蛋白质中的120个SH2结构域进行了多序列比对。从蛋白质数据库(PDB)中提取了200多个蛋白质结构:包括66个基于核磁共振(NMR)的结构和153个来自X射线晶体学实验的结构。鉴于结合位点构象的变异可能显著影响其结合特性,所有文件被拆分为单个结构,最终共计1633个结构。
关键药效团相互作用点:pTyr结合口袋、结合位点中心的羰基氧原子、疏水亚口袋。
基于结合位点中心12 Å范围内的溶剂可及分子表面计算了基于形状的数值描述符。根据3D形状相似性对三维结构进行聚类。筛选出8个空间差异显著的结构用于分子对接。
| Cluster No. | Centroid structure (PDB id, chain, NMR model) | Centroid structure: organism, gene, domain | Structures in cluster |
|---|---|---|---|
| 1 | 1o49, chain A | Homo Sapiens SRC SH2 | 223 |
| 2 | 2fci, chain A, model 6 | Bos Taurus PLCG1 SH2-2 | 48 |
| 3 | 2ge9, chain A, model 15 | Homo Sapiens BTK SH2 | 72 |
| 4 | 3in7, chain A | Homo Sapiens GRB2 SH2 | 183 |
| 5 | 2jyq, chain A, model 9 | Homo Sapiens GRB2 SH2 | 114 |
| 6 | 2k7a, chain B, model 5 | Mus Musculus ITK SH2 | 218 |
| 7 | 2kk6, chain A, model 14 | Homo Sapiens FER SH2 | 149 |
| 8 | 1uus, chain A | Dictyostelium Discoideum DSTA SH2 | 129 |
针对Stat3beta的虚拟筛选:
• 合作方:纽约医学院,Gyeong Baeg
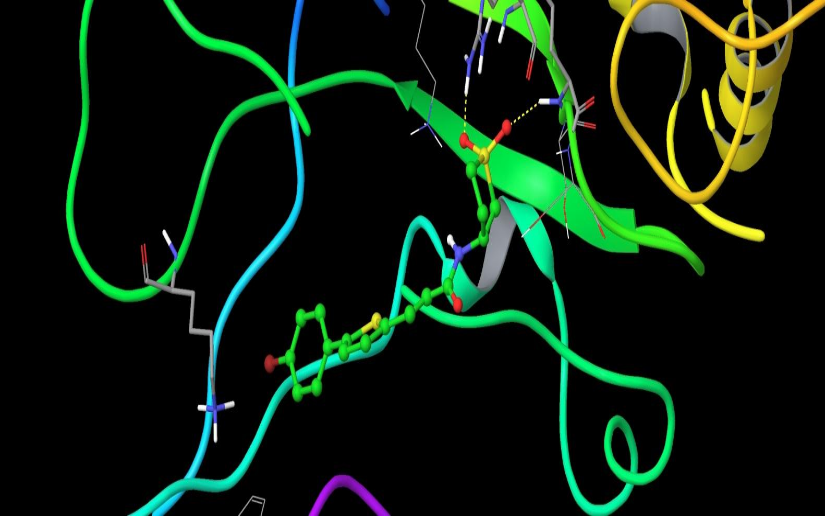
化合物在尺寸上显著小于与该靶点相互作用的天然肽。因此,在构建化合物库时,我们尝试填充酪氨酸磷酸化结合位点附近所有可能的子口袋。蛋白的整个可利用表面被有条件地划分为5个模型,并在此基础上进行了对接后的分析。举例而言,前两个模型是:
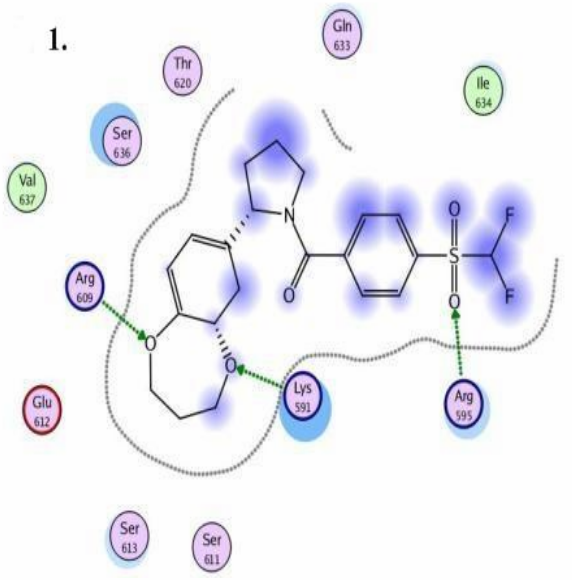





 很棒
很棒

 |
|